- DNS Polymerase III
-
Die DNA-Polymerase III ist ein Enzym, welches die Synthese von DNA aus Desoxyribonukleotiden an einer DNA-Matrize katalysiert. Das Holoenzym spielt die wichtigste Rolle bei der prokaryotischen DNA-Replikation. Wichtigste Merkmale sind seine vielen Untereinheiten und die sehr hohe Katalysatorwirkung, Genauigkeit und Prozessaktivität (Fähigkeit eines Enzyms viele Reaktionen hintereinander zu katalysieren ohne das Substrat zu verlieren). Neben DNA-Polymerase III sind auch noch zwei weitere DNA-Polymerasen in Prokaryoten bekannt.
Inhaltsverzeichnis
Funktion
Die DNA-Polymerase III knüpft mehrere tausend Phosphordiestherbindungen mit seinem Substrat bevor es dieses verlässt. Somit kann sie die Matrize festhalten und erst nach der vollständigen Replizierung wieder entlassen. Des weiteren verfügt die DNA-Polymerase III über eine starke Katalysatorwirkung die es ihr ermöglicht pro Sekunde 1000 Nukleotide anzufügen. Diese starke Katalysatorleistung ist damit zu erklären, dass sie sich nicht vom Substrat lösen muss wie z. B. DNA-Polymerase I. Der neue Strang wächst in 5' − > 3' Richtung. Außerdem ist es der DNA-Polymerase III möglich 3' − > 5' Korrektur zu lesen und falsch eingebaute Nukleotide zu ersetzen.
Aufbau
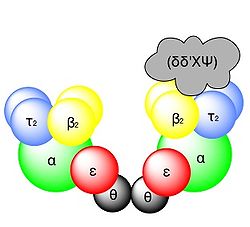
Das Holoenzym ist verglichen mit der DNA-Polymerase I um eine Zehnerpotenz schwerer und das Molekülmasse liegt bei fast 900 kD. Das Enyzm ist als asymmetrisches Dimer aufgebaut, um beide Elternstränge am selben Ort zur gleichen Zeit zu replizieren. Die Asymmetrie rührt daher, dass Leit- und Folgestrang unterschiedlich synthetisiert werden.
Die α-Untereinheit ist die Polymerase und die ε ist die 3' − > 5'-Exonuklease für das Korrekturlesen. Beide sind katalytisch aktiv aber nicht prozessiv, das übernehmen die Untereinheiten β2 und τ2. Die Prozessivität lässt sich durch die Raumstruktur von β2 erklären. Diese Untereinheit bildet einen Ring durch den der DNA-Doppelstrang hindurchgleitet und so sich nicht vom Substrat trennen muss.
Synthese
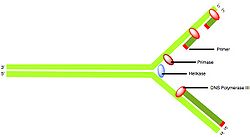
Die ATP-betriebene Helikase entwindet den DNA-Doppelstrang und ermöglicht die Nutzung beider Stränge als Matrize. Es wird gleichzeitig der Leit- und der Folgestrang synthesiert, jedoch nicht in derselben Art und Weise. Das Holoenzym beginnt mit dem Leitstrang, indem der von der Primase gesetzte Primer gebunden wird und synthetisiert diesen kontinuierlich. Der Folgestrang wird viel komplizierter synthetisiert, weil dieser von 5' − > 3' verläuft und eine Synthese nicht von 3' − > 5' verlaufen kann. Daher wird er in Fragmenten synthetisiert, was in vielen einzelnen 5' − 3' Synthesen resultiert. Die Fragmente werden auch Okazaki-Fragment genannt. Ein Fragment ist immer ein zu einer Schleife gewundener Teil des DNA-Einzelstranges, das im aktiven Zentrum der α-Untereinheit ist und in derselben Richtung läuft wie der Leitstrang. Nach ca. 1000 Nucleotiden wird der Folgestrang entlassen und die nächste Schleife in das aktive Zentrum geführt, dazu setzt die Primase wieder einen Primer. Die entstehenden Lücken werden durch die DNA-Polymerase I aufgefüllt, da der DNA-Polymerase III die Reparaturfunktion 5' − > 3' fehlt. Außerdem werden die RNA-Reste der Primer entfernt.
Quellen
- Berg, Jeremy M.; Tymoczko, John L.; Stryer, Lubert: Biochemie, Berlin/Heidelberg 2003 ISBN 3-8274-1303-6
- Madigan, T. Michael; Martinko, M. John; Parker, Jack: Biology of Microorganisms, London 2003 ISBN 0-13-066271-2
Wikimedia Foundation.