- Pseudoknoten
-
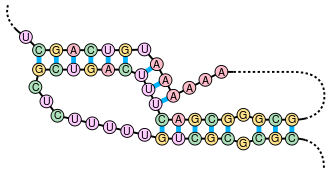 Dieses Beispiel eines natürlich vorkommenden Pseudoknotens ist in der RNA-Komponente der menschlichen Telomerase zu finden. Sequenz aus [1].
Dieses Beispiel eines natürlich vorkommenden Pseudoknotens ist in der RNA-Komponente der menschlichen Telomerase zu finden. Sequenz aus [1].
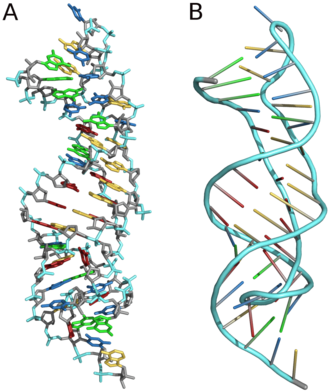 Räumliche Darstellung eines Pseudoknots einer menschlichen Telomerase-RNA. (A): Stäbchenmodel. (B) RNA-Rückgrat. Den beiden Abbildungen liegt die pdb-Datei PDB 1YMO und das Farbschema aus Ribonukleinsäure zugrunde.
Räumliche Darstellung eines Pseudoknots einer menschlichen Telomerase-RNA. (A): Stäbchenmodel. (B) RNA-Rückgrat. Den beiden Abbildungen liegt die pdb-Datei PDB 1YMO und das Farbschema aus Ribonukleinsäure zugrunde.
Ein Pseudoknoten ist eine RNA-Sekundärstruktur, die aus zwei Haarnadelstrukturen besteht, wobei die Schleife eines Stammes einen Teil des zweiten bildet. Pseudoknoten wurden das erste Mal 1982 in einem Mosaikvirus (TYMV, turnip yellow mosaic virus) entdeckt.[2] Pseudoknoten falten sich in knotenförmige dreidimensionale Gebilde, die aber keine echten topologische Knoten darstellen.
Vorhersage und Erkennung
Pseudoknoten können durch übliche Vorhersagemethoden für Sekundärstrukturen wie Mfold und Pfold nicht immer als solche erkannt werden, da sich die Positionen der Basenpaarungen in der Sequenz überlappen können. Die Standardmethoden der dynamischen Programmierung erkennen gepaarte Haarnadelstrukturstämme mittels rekursiver Bewertungssysteme und können folglich nur korrekt geschachtelte, überlappfreie Basenpaarungen erkennen. Auch mit den neuen Methoden der stochastischen kontextfreien Grammatiken ist eine Erkennung unmöglich. Sie erkennen lediglich den stabileren der beiden Pseudoknoten-Stems.
Es ist möglich, dass in einigen Situationen Methoden ähnlich der dynamischen Programmierung Pseudoknoten erkennen können, aber diese sind im Allgemeinen sehr ineffizient.[3] Für das allgemeine Problem der Pseudoknoten-Vorhersage wurde bewiesen, dass es NP-vollständig ist.[4]
Biologische Bedeutung
Einige wichtige biologische Prozesse basieren auf RNA-Molekülen, die Pseudoknoten bilden. Beispielsweise beinhaltet die menschliche Telomerase einen Pseudoknoten, der essentiell für die Aktivität des Enzyms ist.[1]
Referenzen
- ↑ a b Chen, JL. und Greiger, CW. (2005): Functional analysis of the pseudoknot structure in human telomerase RNA. In: Proc Natl Acad Sci USA 102(23); 8080–8085; PMID 15849264; PDF (freier Volltextzugriff, engl.)
- ↑ Staple, DW. und Butcher, SE. (2005): Pseudoknots: RNA structures with diverse functions. In: PLoS Biol 3(6); e213; PMID 15941360; PDF (freier Volltextzugriff, engl.)
- ↑ Rivas, E. und Eddy, SR. (1999): A dynamic programming algorithm for RNA structure prediction including pseudoknots.. In: J Mol Biol, 285(5); 2053–2068; PMID 9925784; doi:10.1006/jmbi.1998.2436
- ↑ Lyngsø, RB. und Pedersen, CN. (2000): RNA pseudoknot prediction in energy-based models. In: J Comput Biol 7(3–4): 409–427; PMID 11108471; PDF (freier Volltextzugriff, engl.)
Wikimedia Foundation.
