- Transspleißen
-
Als Transspleißen wird das Zusammenfügen von Exons verschiedener mRNAs bezeichnet. Im Gegensatz zum normalen cis-Splicing werden hier also Exons unterschiedlicher RNAs, die aber vom selben Gen stammen können, miteinander verknüpft. Das „klassische“ trans-Splicing tritt bei Trypanosomen und Nematoden auf, daneben wurden einige Fälle von trans-Splicing beim Menschen entdeckt.
„Klassisches“ trans-Splicing in Trypanosomen und Nematoden
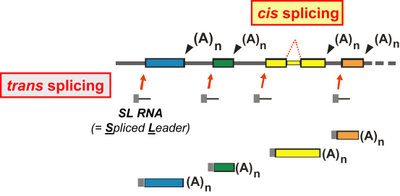 Übersicht über das Prozessieren der prä-mRNA in Trypanosomen. Neben dem cis-Splicing (nur ein bekanntes Intron, vgl. Text) tritt hier vor allem trans-Splicing auf, bei dem ein so genanntes Mini-Exon der Spliced-Leader-RNA (SL-RNA) (als grauer Kasten dargestellt) mit einem Exon eines polycistronischen Transkripts (bunte Kästen) verknüpft wird. Hier werden also zwei unterschiedliche RNAs miteinander „in trans“ gespleißt, was für den ganzen Prozess namemsgebend ist. Schließlich setzt die Polyadenylierung die fertige mRNA mit dem Poly(A)-Schwanz (dargestellt als A(n)) frei.
Übersicht über das Prozessieren der prä-mRNA in Trypanosomen. Neben dem cis-Splicing (nur ein bekanntes Intron, vgl. Text) tritt hier vor allem trans-Splicing auf, bei dem ein so genanntes Mini-Exon der Spliced-Leader-RNA (SL-RNA) (als grauer Kasten dargestellt) mit einem Exon eines polycistronischen Transkripts (bunte Kästen) verknüpft wird. Hier werden also zwei unterschiedliche RNAs miteinander „in trans“ gespleißt, was für den ganzen Prozess namemsgebend ist. Schließlich setzt die Polyadenylierung die fertige mRNA mit dem Poly(A)-Schwanz (dargestellt als A(n)) frei.
Kinetoplastida, zu denen unter anderem die Erreger der Schlafkrankheit, Chagas-Krankheit und Nagana zählen, insbesondere Trypanosoma brucei brucei, sind die klassischen Modellorganismen für das trans-Splicing im engeren Sinne. Diese Organismen produzieren bei der Transkription ähnlich den Bakterien ein polycistronisches Transkript, aus dem einzelne Gene durch das trans-Splicing freigesetzt werden. Diese Reaktion findet in einem speziellen Typ von Spliceosom statt, bei dem der U1-snRNP durch den so genannten „Spliced-Leader“ (SL) snRNP ersetzt wird. Anders als die U1-snRNA wird die spliced-leader-RNA allerdings in der Splicing-Reaktion verbraucht, da ihr 5'-Ende ein Miniexon enthält, das zusammen mit dem Exon des polycistronischen Transkripts später die mRNA ausmacht (vergleiche nebenstehende Abbildung). Das Miniexon der SL-RNA enthält weiterhin den AUG-Startcodon, es ist also essentiell für eine vollständige mRNA mit korrektem open reading frame.
Neben dem trans-Splicing wurde in Trypanosomen nur ein einziges „klassisches“ cis-Intron im Gen für die Poly-A-Polymerase entdeckt, was bedeutet, dass auch Trypanosomen einen U1-snRNP enthalten, jedoch nur in äußerst geringen Mengen (dieser wurde auch kürzlich charakterisiert).
Trans-Splicing im engeren Sinne wurde auch bei Nematoden und Ciona intestinalis beobachtet, es fehlt jedoch in fast allen anderen Organismen.
Trans-Splicing im Menschen
Auch im Menschen wurden einige Fälle des trans-Splicings berichtet. Anders als bei Trypanosomen existiert hier jedoch kein Spliced-Leader-snRNP, also kein trans-Splicing im „klassischen“ Sinne. Vielmehr werden hier zwei prä-mRNAs des gleichen Gens miteinander prozessiert, die sich in allen bisher berichteten Fällen in ihrer Sequenz nicht voneinander unterscheiden (daher auch trans-Splicing, weil zwei unabhängige RNAs miteinander gespleißt werden). Dies resultiert in einer Duplikation eines Exons in der späteren mRNA. Allerdings tritt dieser Prozess im Menschen nur äußerst selten auf (aktuelle Zahlen sprechen von zwei „echten“ Beispielen, die nur mit 15 ESTs in den Datenbanken zu finden sind), dennoch aber lösten die Berichte eine heiße Diskussion aus, ob unter Ausnutzung dieses Prozesses nicht Wege gefunden werden könnten, erblich bedingte Erkrankungen zu therapieren (erste Anstrengungen dazu wurden bereits beim Tau-Gen unternommen, das bei Demenzen wie der Alzheimer-Krankheit eine Rolle spielt). Auch hier findet sich aber – wie auch bei einer Vielzahl weiterer innovativer, aber auch bei lange bekannten Therapiestrategien – das Problem der delivery des ‚Wirkstoffs‘, der in diesem Fall eine RNA darstellt.
Auch in Cyanobakterien (vgl. Artikel Intein, letzter Absatz) spielt Transspleißen eine Rolle.
Referenzen
Wikimedia Foundation.
